Hippo's data
ch2지도학습_분류classification의 선형모델 linear_model 본문
ch2지도학습_분류classification의 선형모델 linear_model
Hippo's data 2023. 9. 10. 18:30오늘은 저번에 이어서 지도학습 중 선형모델에 대해 알아보겠습니다
저번에는 회귀방식의 선형모델을 알아보았는데요
이번에는 분류 방식의 선형모델 실습을 해보도록 하겠습니다
분류용 선형모델은 이진분류Binary Classification와 다중분류Multiclass Classification로 구분할 수 있습니다
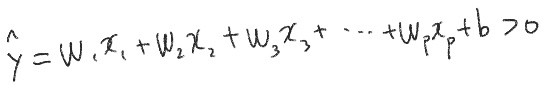
-> 임계치 0과 비교하여 방정식 값이 0보다 작으면 -1 / 크면 +1로 예측
대중적인 알고리즘
-> 로지스틱회귀 logistic regression / linear_model.LogisticRegression에 구현됨
-> 서포트 벡터 머신 support vector machine / svm.LinearSVC에 구현됨
*** 주의) 로지스틱회귀 logistic regression -> 회귀 regression 이름이 들어가지만 분류알고리즘
# 이진분류 Binary Classification

-> forge데이터 셋 사용 / LinearSVC, LogisticRegression 적용
-> 두모델 비슷한 결정경계만듦 / 똑같이 두개 데이터 잘못분류
-> 두모델 모두 기본적으로 L2규제 사용함 -> 규제강도 매개변수 : C(기본값 1.0)

-> C 커지면 규제 감소(모델복잡도 증가) = 훈련세트 학습 많이함 / 개개의 데이터 포인트 정확히 분류하려함(특정 데이터)
-> C 작아지면 규제 증가(모델복잡도 감소) = W가중치값 0에 가까워지게함 / 데이터 포인트 중 다수에 맞추려함(일반화)
*** 선형모델 - 회귀에서는 alpha값 커지면 규제 증가(모델 복잡도 감소) -> C와 반대
->훈련 세트 점수: 0.958 / 테스트 세트 점수: 0.958
-> 유방암 데이터셋 사용 load_breast_cancer / 기본값 C=1
-> 훈련, 테스트 세트 성능 0.95로 좋지만 서로 비슷 => 과소적합 추정
-> 훈련 세트 점수: 0.981 / 테스트 세트 점수: 0.965
-> C =100 => 훈련, 테스트 성능 둘다 조금 더 상승 -> C값 키우며 모델 복잡도 높임
-> 훈련 세트 점수: 0.953 / 테스트 세트 점수: 0.951
# C =0.01 => 기본매개변수 C =1보다 정확도 낮아짐
# 이미 과소적합된 모델에서 더 모델 복잡도 낮춤 -> 정확도 더 떨어짐

-> 매개변수 C에 따른 w계수값의 변화관찰
-> C값이 작을수록 W계수값 범위가 줄어듬(0에 가까워짐)
-> 로지스틱 회귀 logistic reg -> 기본적으로 릿지 사용(L2규제) -> w계수값 완전히 0되지 않음
-> 3번째 특성 'mean perimeter' -> C값이 작아졌지만 w계수값의 범위(절댓값)가 오히려 커짐
-> w계수 클래스와 특성의 연관성 주의 -> 세번째 특성 'mean perimeter'은 양성이나 악성 신호 모두 될수 있음 - 두 클래스 둘 다 연관성 가질 수 있음 (다른 샘플은 악성샘플만 연관성있음 - 한 클래스 가짐)
-> 선형모델 계수는 항상 의심하고 조심해서 해석하기 (특정 특성이 두 클래스 모두와 관련있을 수 있으므로)

-> C=0.001 인 l1 로지스틱 회귀의 훈련 정확도: 0.91
C=0.001 인 l1 로지스틱 회귀의 테스트 정확도: 0.92
C=1.000 인 l1 로지스틱 회귀의 훈련 정확도: 0.96
C=1.000 인 l1 로지스틱 회귀의 테스트 정확도: 0.96
C=100.000 인 l1 로지스틱 회귀의 훈련 정확도: 0.99
C=100.000 인 l1 로지스틱 회귀의 테스트 정확도: 0.98
-> 라쏘(L1규제)사용 -> w계수 0값 가능 -> 일부특성만 이용 가능
-> LinearSVC (서포트 벡터 머신) -> loss 매개변수-> 손실함수 지정가능(기본값 : squred_hinge -> 제곱힌지손실)
*** 힌지손실hinge loss 이란?
-> 분류모델에서 주로 사용되는 손실함수loss function / 특히 서포트 벡터 머신 SVM에서 사용
-> 힌지손실 hinge : penalty매개변수에 L2(릿지)만 가능
-> 제곱힌지손실 squared_hinge : 힌지손실에 이상치에 더 많은 패널티 부과 / penalty매개변수에 L1(라쏘) / L2(릿지) 둘다 가능
힌지 hinge = 경첩 ( 함수가 경첩 구조를 닮음)
서포트 벡터 머신 SVM의 목적 -> 데이터를 잘 구분하는 마진margin 을 최대한 크게 하기
힌지 손실의 목적-> 마진 바깥 관측값은 손실을 무시(loss = 0) / 마진 내 관측값 손실 크게 함
*** 주의) LogisticRegression -> penalty매개변수에 L1/L2/elasticnet/None(규제 없음)가능 / 이외에도 다양한 매개변수값 변경이 가능함(solver = 'saga' / 'liblinear' 등등)
***경첩그림

*** 힌지 손실 함수 hinge loss function
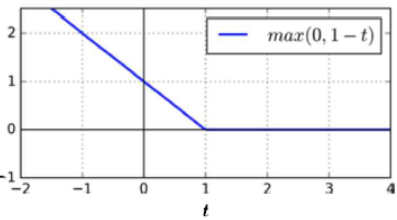
*** 서포트 벡터 머신 SVM의 마진margin

# 다중분류 Multiclass Classification (클래스 3이상으로 분류)
선형분류모델은 대부분 이진분류 지원함 (로지스틱 회귀 제외)
즉, 선형분류모델은 대부분은 다중분류 지원하지 않는다
그렇다면 다중분류는 어떻게 수행해야할까?
이진분류를 다중분류로 확장하는 기법 : 일대다 방법 ( one vs rest 혹은 one vs all)
-> 클래스 수만큼 이진분류 모델 만듦 예) 3개 분류 -> 이진분류r 3
-> 각 클래스마다 w계수,b절편 가짐

-> 모든 이진 분류기 중 함수의 가장 높은 값을 내는 분류기 클래스를 예측 값으로 선택

-> 세 클래스 가진 2차원 데이터에 Linear SVC(Linear Support Vector Classifier) 훈련
-> 계수 배열의 크기: (3, 2) / 절편 배열의 크기: (3,) -> 세클래스로 분류하므로 계수, 절편 3개
-> coef_ 행 -> 세 클래스 대응하는 w계수벡터 / 열 -> 각 특성에 따른 w계수값(이 데이터셋에서는 2개 가짐)
-> intercept_ -> 각 클래스 절편 (1차원 벡터)
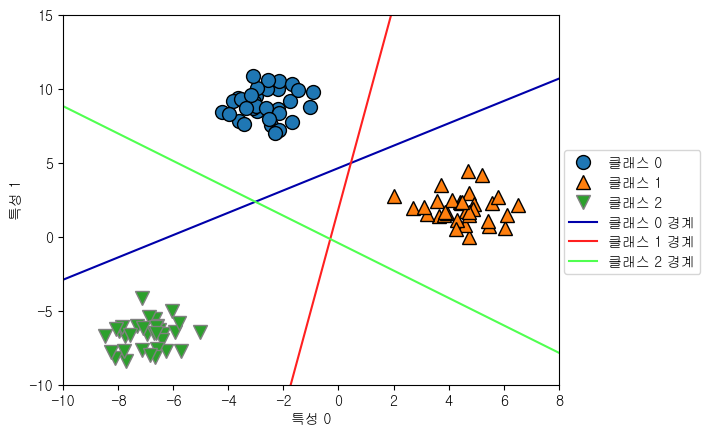
-> 세 이진 분류기가 만드는 경계 시각화

-> 다중 클래스 분류기의 결정경계표현
-> 분류공식 결과가 가장 높은 클래스로 분류함(가장 가까운 직선의 클래스로 분류)
# 선형모델 linear model 정리
<선형모델 주요 매개변수>
-> 회귀 모델 => alpha -> alpha값 클수록(규제 강하게) 모델 단순
-> 분류 모델 - LinearSVC, LogisticRegression => C -> C값 작을수록(규제 약하게) 모델 단순
-> alpha, C -> 로그 스케일로 최적치 결정 (보통 0.01 /0.1 /1/ 10 -> 10배씩 적용)
-> 이후 L1(릿지) / L2(라쏘) 규제 사용할지 정함
-> 중요특성 많다 -> L2 / 적다 -> L1
<선형모델 장점>
-> 학습, 예측빠름 / 큰데이터셋, 희소데이터 셋 잘 작동 / 어떻게 예측 만들어지는지 쉽게 이해 가능 / 샘플에 비해 특성 많을 때 잘 작동함 (고차원 모델)
but 저차원 -> 다른 모델이 일반화 성능 더 좋음
<대용량 데이터 빠르게 처리방법>
-> LogisticRegression, Ridge에 solver='sag' 옵션 지정
*** sag
-> Stochastic Average Gradient descent(확률적 평균 경사 하강법)
-> 반복 진행할 때 이전 모든 경사 평균 사용하여 계수 갱신함
혹은
-> 선형모델 SGDClassifier / SGDRegressor 사용
# 번외) 메서드 연결 method chaining
-> 모델 객체생성 / 훈련, 예측 한줄입력
-> 코드 짧게 작성 바람직하지 않음 -> 코드 읽기(해석하기) 어려워짐
-> 학습된 모델 변수에 남지 않음(예측 결과만 담은 변수만 남음) -> 새 데이터 예측 불가능
'ML(Machine Learning) > 책: 파이썬 라이브러리를 활용한 머신러닝(2판)' 카테고리의 다른 글
| ch2지도학습_나이브베이즈 분류기 Naive bayes classifier (0) | 2023.09.10 |
|---|---|
| ch2지도학습_회귀regression의 선형모델 linear_model (0) | 2023.09.08 |
| ch2지도학습_K-최근접이웃 K-Neareset Neighbors(K-NN) (2) | 2023.09.07 |
| ch1 붓꽃(iris) 품종분류예제 (2) | 2023.09.05 |



